Le lysozyme est une enzyme de la classe des hydrolases, rencontrée dans les sécrétions nasales, lacrymales et salivaires. Elle coupe (hydrolyse) les polysaccharides des parois des cellules bactériennes. La structure Rastop permet de révéler des détails au niveau du site actif de l'enzyme.
الليزوزيم هو إنزيم من فئة الهيدرولاز (الحلمئيات)، ويوجد في إفرازات الأنف والدموع واللعاب. يحلل إنزيم ليزوزيم السكريات من جدران الخلايا البكتيرية. يتيح برنامج Rastop الكشف عن التفاصيل على مستوى الموقع النشيط للإنزيم.
Lysozyme is an enzyme of the hydrolase class, found in nasal, tear and salivary secretions. It cuts (hydrolyzes) the polysaccharides from the walls of bacterial cells. The Rastop structure makes it possible to reveal details at the level of the active site of the enzyme.
Ce projet d'étude de la relation Structure-Fonction des molécules est consacré au lysozyme sous sa forme complexée à un inhibiteur (Code 1JEF). Une copie est disponible peut
être conservée sur CD.
Chaque étudiant choisira la protéine qu'il désire étudier à l'aide du programme RasTop. En exploitant les connaissances de base sur la protéine, l'étudiant préparera un compte-rendu de 4-5 pages décrivant en détail la structure de la molécule. Un index contenant au moins 3-6 images RasTop peut être joint au compte-rendu. Joindre au compte-rendu une copie des
informations de base sur la molécule sujet d'étude ainsi que des références bibliographiques. Les images peuvent être fourni sous format zip et envoyées par E-mail à
votre Professeur.
Le compte-rendu doit fournir les informations suivantes:
1/ Information de base sur la protéine (fonction de la protéine, son rôle, lieux de synthèse et lieu d'activité,...).
2/ structure de la protéine (nombre de sous-unités,
structure secondaire,...).
3/interactions moléculaires importantes dans la fonction de la
protéine (images RasTop à l'appui). Les interactions concernent,
entre autres, les liaisons hydrogène et électrostatique
et les interactions hydrophobes.
Pour le cas du lysozyme l'Etudiant trouvera les meilleures illustrations
visualisant toute l'information sur cette enzyme. Plusieurs questions
peuvent être posées dont:
1/ Combien de cystéines contient le lysozyme ?
2/ Combien de ponts dissulfures contient la molécules. Entre
quels acides aminés sont ils formés?
3/Identifier les acides aminés qui entourent le substrat
logé dans le site actif
4/ Mesurer les distances entre le lieux de coupure du substrat
et les acides aminés Glu35 et Asp52
Quelques informations sur le lysozyme.
Le lysozyme est une hydrolase rencontrée dans les sécrétions
nasales, lacrymales et salivaires. Elle hydrolyse les polysaccharides des parois des cellules bactériennes.
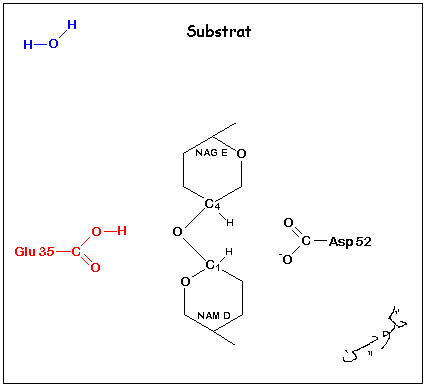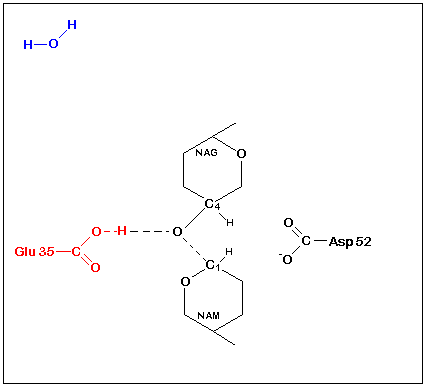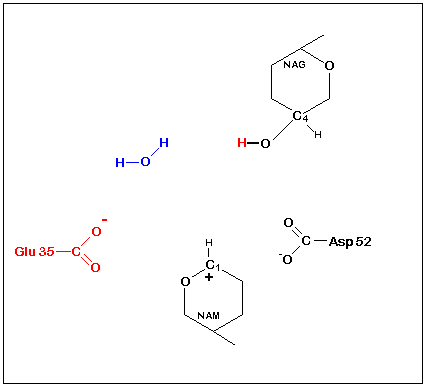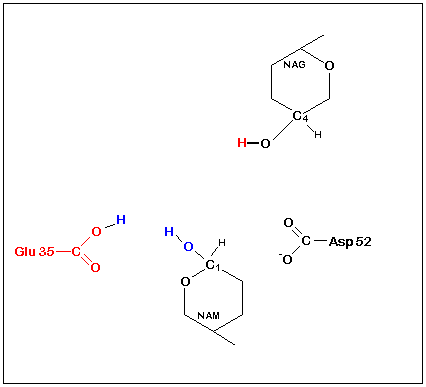
Le lysozyme est constitué d'une seule chaîne polypeptidique de 129 acides aminés qui lui donnent par repliement la forme de 'grain de blé gonflé'. Le substrat, un polysaccharide composés d'unités
alternées de N-acétylglucosamine (NAG) et d'acide N-acétylmuramique (NAM), se loge dans une crevasse située sur un côté de la molécule (site
actif-structure). l'enzyme catalyse la rupture de la liaison glycosidique du substrat NAG-NAM (fig. ci contre) unissant les deux résidus. Les acides aminés Asp52 et Glu35, se trouvant chacun à 0,3 nm de la liaison NAG-NAM, vont servir de donneurs ou d'accepteurs
de protons. Asp52 étant dans un environnement polaire, est ionisé au pH optimal du lysozyme (pH 5,0). Glu35, se trouvant dans une région non polaire, n'est pas ionisé. Le mécanisme est le suivant:
Le carboxyle du Glu35 donne un proton coupant la liaison C1-O et libérant NAG. Le Carbocation qui en résulte en C1du NAM est stabilisé par la charge négative d'Asp52. Lcarbocation réagira ensuite
avec OH- de l'eau en libérant NAM puis Glu35 est reprotoné et le cycle recommence (catalyse acide).
Dans certaines publications, on peut noter que la liaison du polysaccharide
avec l'enzyme se fait par le biais de 14 liaisons
hydrogènes contractées par les radicaux libres des acides aminés dont Arg114, Asn37, Asn44, Trp62, Trp63, Asp101 et Gln57
LYSOZYME. STRUCTURE PAR RASTOP
1/Le fichier du travail porte la référence LYSOZYME EI_moldraw2c76285b (Code 1JEF) montrant l'enzyme liée à un inhibiteur (analogue de substrat. Une copie est disponible sur votre CD (dans le répertoire MOLECULES DATA (CD)). Une fois le fichier (format pdb) est ouvert par RasTop, il donne une image semblable à celle ci contre (après avoir tapé
la commande 'set backgound white' dans la fenêtre des commandes
RasMol minimisée au bas de votre écran, voir
explications).
Pour tourner la molecules dans tous les sens, maintenez enfoncé le bouton
gauche de de la souiris tout en la glissant dans un sens ou l'autre.
Pour effectuer un zoom, maintenir enfoncée la touche shift (î) tout en déplaçant la souris sur la position bouton gauche enfoncé.
Pour avoir des informations sur la molecule saisissez 'show information' ou 'show sequence' dans la boite des commandes de RasMol, puis valider par la touche entrée.
Pour étudier le site actif et son environnement, vous pouvez partir du départ en chargeant la molécule et rendre le fond de l'mage blanc au lieu du noir (set background white). On obtient l'image ci dessous:
On peut ensuite sélectionner le faux substrat pour bien situer le site actif de l'enzyme.
Pour localiser le ligand (inhibiteur) saisissez 'select ligand' dans la boîte des commandes et valider par la touche entrée.
Pour avoir d'autres information sur la molécule comme le nombre de Cystéines et après avoir visualisé la molécule sous 'sticks', on peut selectionner toutes les cystéines de la molécules en composant dans la fenêtre des commandes:
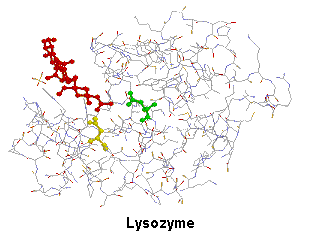
- select cys, On obtient l'image ci contre (LysozymeCys).
Pour sauvegarder cette image (format gif) sur le disque dur de votre ordinateur (avec un nom lysozymeCys.gif), choisir dans 'Export' 'GIF' ou saisissez "write lysozymeCys.gif" dans la boîte des commandes RasMol.
Pour affecter une couleur (ex. rouge) au ligand saisissez encore 'color red' et validez. Pour le distinguer des autres motifs sélectionnez 'ball & stick' dans le menu DISPLAY . Pour selectionner les acides aminés Asp52 et Glu35, on saisira successivement dans la fenêtre des commandes RasMol:'select Asp52', 'color yellow' (jaune) (mettre ensuite display ball & stick), 'select Glu35', 'color green' (vert) (mettre ensuite display ball & stick)




LYSOZYME. STRUCTURE PAR Rastop (suite)
On peut avoir un autre aperçu sur le positionnement du ligand par rapport aux acides aminés de contact du site actif.
On peut mesurer les distances en Angstrum entre le ligand et les deux acides aminés Glu35 et Asp52 en saisissant dans la fenêtre des commandes:
- set picking monitor suivie de clicks sur les 2 éléments entre lesquels on mesure la distance. Cela donne l'image ci dessous. On n'oublie pas de s'aisir:
- set picking ident pour désactiver le marquage et passer aux étapes suivantes
PROJETS DE MOLECULES ETUDIES PAR RasTop
PROJET
'HEMOGLOBINE' (Tutorial):
- STRUCTURE 1: hemoglobine-structure-rastop-1.html
- STRUCTURE 2: hemoglobine-structure-rastop-2.html
- STRUCTURE 3: hemoglobine-structure-rastop-3.html
- STRUCTURE 4: hemoglobine-structure-rastop-4.html
PROJET 'LYSOZYME': - LYSOZYME (Complexe):
PROJET 'TRANSAMINASES':
- ASPARTATE AMINOTRANSFERASE (Complexe)
PROJET 'PEROXYDASES':
- PEROXYDASE (Complexe)
-
Programme Rastop. Préambule
- Hémoglobine. Structure par JMOL

360 pages, 2018, ISBN : 978-9920-35-345-8 + DVD mis à jour + Assistance.

306 pages, 2013, ISBN : 978-99-54-32-663-3 + DVD mis à jour 2018 + Assistance
Comment avoir ces livres ? - أين يمكن اقتناء الكتب؟
Chaine Youtube (abonnement). Vidéos multilingues

-
من علوم الحياة إلى البيوكيمياء
Des Sciences de la vie au Lycée à la Biochimie à l'Université
-
تحميل ملفات في مواضيع البيوكيمياء
Téléchargement de fichiers en Biochimie
Afin de pouvoir continuer à servir les visiteurs, soutenez nos actions sur le site takween en faisant acquisition des ouvrages et supports pédagogiques desitinés à améliorer l'enseignement et la recherche scientfique en Biochimie.